-
云南松毛虫( Dendrolimus houi Lajonquiere)又名大柏毛虫,属鳞翅目(Lepidoptera)枯叶蛾科(Lasiocampidae)松毛虫属( Dendrolimus ),主要危害柏木、柳杉、思茅松和马尾松等针叶树种[1]。该虫严重威胁森林生态安全及林业可持续发展[2],因此我国对于其生物学特性、防治和管理等方面都有了较为深入的研究。孔祥波[3]等人鉴定了云南松毛虫的性信息素包括E5,Z7-12:OH和E5,Z7-12:OAc两种成分,成功应用于林间种群动态监测。关于松毛虫属内近缘种之间亲缘关系的研究也获得了较大成果。2004—2015年期间多种分子标记被应用于松毛虫属内亲缘关系的研究[4-10],综合不同的分子标记获得了一个相似的结果,云南松毛虫与思茅松毛虫亲缘关系较近,马尾松毛虫、文山松毛虫、德昌松毛虫、油松松毛虫、赤松毛虫和落叶松毛虫亲缘关系相对较近。
线粒体基因组(mtDNA)是一种双链闭环状的DNA分子,在鳞翅目昆虫体内编码结构稳定,可操作性强,进化速率快[11-12],近年来被广泛应用于解释物种间的系统发育关系[13-14]。松毛虫属近缘种昆虫(马尾松毛虫NC_027156.1,赤松毛虫KJ_913815,油松毛虫KJ_913817,思茅松毛虫MF100138.1)已经完成了线粒体基因组的测序,但并未见云南松毛虫的报道。本研究通过高通量测序获得云南松毛虫的线粒体全基因组序列,并结合已报道的鳞翅目蛾类的线粒体基因组进行比较分析,探究松毛虫所在的高级阶元的分类地位,以期丰富云南松毛虫线粒体全基因组的基础数据,为松毛虫属系统学和分类学的研究提供更准确的分子生物学数据。
-
云南松毛虫于2016年9月采自云南省景东县(23°56′N,101°15′E),采集到的活体昆虫固定在无水乙醇中,置-20℃冰箱保存备用。样本由中国林业科学研究院孔祥波老师鉴定。
-
上海美吉生物公司对云南松毛虫样品本进行DNA提取,使用Covaris M220超声破碎,DNA片段化为400~500 bp。制备DNA文库,扩增后将符合要求的文库安排Illumina Hiseq仪器进行paired-end(PE)测序。将获得的原始序列进行质控,利用SOAPdenovo v2.04拼接软件对质控后的数据进行de novo组装,将组装得到的contig与线粒体数据库进行比对,筛选得到来自线粒体的contig;然后利用MITObim v1.6迭代比对,将测序的所有clean reads mapping于contig上延伸,通过gap close获得线粒体的全基因组序列。利用DOGMA软件对基因组中包含的gene、rRNA和tRNA进行预测。确定无误后上传至NCBI数据库。
-
云南松毛虫线粒体基因组全序列使用在线软件提交到NCBI中。采用CGview软件进行线粒体基因组圈图的绘制。在线软件tRNAscan-SE Search Server对tRNA基因二级结构进行预测,两种在线比对结果相似,没有被预测出来的tRNA通过与其近缘种相应的tRNA比对进行人工预测。使用MEGA7.0[15]分析线粒体基因组的碱基组成和密码子使用情况,并分析蛋白质编码基因的氨基酸使用情况和相对同义密码子的相对使用度。
-
采用Mega7.0软件基于鳞翅目13科32种蛾类昆虫线粒体基因组的蛋白编码基因序列(表 1),以双翅目Diptera实蝇科Tephritidae地中海实蝇 Ceratitis capitata 和桃果实蝇 Bactrocera zonata 为外群,使用最大似然法(Maximum Likelihood method,ML)构建系统发育树,采用Bootstrap(1 000次重复)检验系统树各分支节点的置信值。采用Mega7.0软件基于线粒体基因组的13个蛋白编码基因,以家蚕为外群,使用邻接法(NJ)构建松毛虫属内系统发育树,采用Bootstrap(1 000次重复)检验系统树各分支节点的置信值,并基于Kimura-2-parameter(K2P)模型计算松毛虫属内种间的遗传距离。
表 1 用于高级阶元系统发育分析的物种信息
Table 1. Information of species used for phylogenetic analysis
科名 Family 物种 Species 线粒体基因组大小
mt DNA Size/bp(A+T)/% GenBank登录号
GenBank accession no.枯叶蛾科 Lasiocampidae 云南松毛虫 Dendrolimus houi 15 443 80.0 - 马尾松毛虫 Dendrolimus punctatus 15 417 79.5 NC_027156.1 思茅松毛虫 Dendrolimus kikuchii 15 422 79.2 MF100138.1 油松毛虫 Dendrolimus tabulaeformis 15 411 79.5 KJ_913817 赤松毛虫 Dendrolimus spectabilis 15 412 79.3 KJ_913815 落叶松毛虫 Dendrolimus superans 15 417 80.1 NC_039841.1 竹纹枯叶蛾 Euthrix laeta 15 368 80.2 KU870700.1 青黄枯叶蛾 Trabala vishnou guttata 15 281 80.9 KU884483.1 天蛾科 Sphingidae 烟草天蛾 Manduca sexta 15 516 81.8 NC_010266.1 Sphinx morio 15 299 81.1 NC_020780.1 大蚕蛾科 Saturniidae 天蚕 Samia cynthia ricini 15 384 79.7 NC_017869.1 章蚕 Eriogyna pyretorum 15 327 80.8 NC_012727.1 夜蛾科 Noctuidae 小地老虎 Agrotis ipsilon 15 377 81.3 KF163965.1 草地夜蛾 Spodoptera frugiperda 15 365 81.1 KM362176.1 斜纹夜蛾 Spodoptera litura 15 383 81.1 KF701043 毒蛾科 Lymantriidae 舞毒蛾 Lymantria dispar 15 569 79.9 FJ617240.1 黄尾毒蛾 Euproctis similis 15 437 80.2 NC_035886.1 茶毒蛾 Euproctis pseudoconspersa 15 461 79.7 KJ716847.1 尺蛾科 Geometridae 桑尺蠖 Phthonandria atrilineata 15 499 81.0 NC_010522.1 蝙蝠蛾科 Hepialidae Ahamus yunnanensis 15 816 82.3 NC_018095.1 人支蝠蛾 Thitarodes renzhiensis 16 173 81.3 NC_018094.1 蚕蛾科 Bombycidae 桑蟥 Rondotia menciana 15 306 78.8 NC_021962.1 家蚕 Bombyx mori 15 643 81.3 NC_002355.1 野桑蚕 Bombyx mandarina 15 928 81.7 NC_003395.1 灯蛾科 Arctiidae 美国白蛾 Hyphantria cunea 15 481 80.4 NC_014058.1 螟蛾科 Pyralidae 亚洲玉米螟 Ostrinia furnacalis 14 563 80.4 NC_003368.1 舟蛾科 Notodontidae 苹掌舟蛾 Phalera flavescens 15 659 80.9 NC_016067.1 杨扇舟蛾 Clostera anachoreta 15 456 80.7 NC_034740.1 草螟科 Crambidae 小蔗杆草螟 Diatraea saccharalis 15 490 80.1 NC_013274.1 二化螟 Chilo suppressalis 15 395 80.6 NC_015612.1 卷蛾科 Tortricidae 茶小卷叶蛾 Adoxophyes honmai 15 680 80.4 DQ073916.1 梨小食心虫 Grapholita molesta 15 717 80.9 HQ392511.1 双翅目 Diptera 地中海实蝇 Ceratitis capitata 15 980 77.5 AJ242872.1 实蝇科 Tephritidae 桃果实蝇 Bactrocera zonata 15 935 73.4 NC_027725.1 -
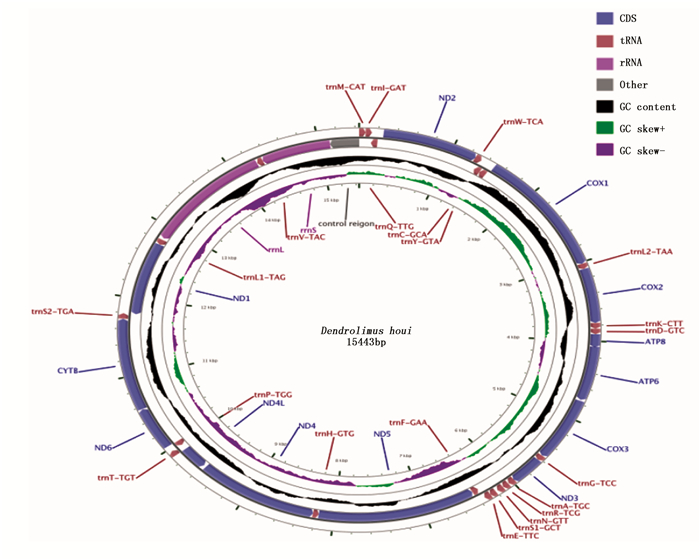
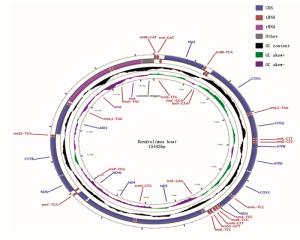
云南松毛虫线粒体基因组全序列总长度为15 443 bp,呈双链闭合环状结构,基因组成包含13个蛋白质编码基因(PCGs)、22个tRNA基因、2个rRNA基因(12S rRNA和16SrRNA),1个A+T富含区(A+T-rich region)(如图 1)。详细注释见表 2。37个基因相邻之间存在基因间隔或基因重叠现象。云南松毛虫线粒体全基因组序列中A、T、C、G的碱基含量分别为41.2%,38.8%,12.4%和7.6%(表 3),表现出明显的AT偏好性。基因组全序列碱基AT-skew值为0.03%,GC-skew值为-0.24%,tRNA基因的AT偏斜和GC偏斜均为正值,rRNA基因的AT偏斜为负,GC偏斜为正。
表 2 云南松毛虫线粒体基因组注释
Table 2. Organization of the mitochondrial genome of Dendrolimus houi
基因
Gene方向
Direction位置
Location长度
Size反密码子
Anticodon起始密码子
Startcodon终止密码子
Stop codon基因间隔
IntergenictrnM F 1 67 67 CAT trnI F 69 132 64 GAT 7 trnQ R 130 198 69 TTG -1 ND2 F 257 1 264 1 008 TTT TAA 58 trnW F 1 263 1 332 70 TCA -2 trnC R 1 325 1 391 67 GCA -8 trnY R 1 393 1 463 71 GTA 0 COX1 F 1 492 3 022 1 531 CGA T 34 trnL F 3 023 3 089 67 TAA 0 COX2 F 3 090 3 771 682 ATA T 0 trnK F 3 775 3 845 71 CTT 0 trnD F 3 847 3 913 67 GTC 3 ATP8 F 3 914 4 075 162 ATT TAA 0 ATP6 F 4 069 4 746 678 ATG TAA -7 COX3 F 4 762 5 550 789 ATG TAA 14 trnG F 5 553 5 618 66 TCC 2 ND3 F 5 619 5 971 353 ATT TA 0 trnA F 5 971 6 038 68 TGC -1 trnR F 6 048 6 112 65 TCG 15 trnN F 6 118 6 184 67 GTT 4 trnS1 F 6 211 6 276 66 GCT 11 trnE F 6 277 6 345 69 TTC -1 trnF R 6 354 6 420 67 GAA 4 ND5 R 6 425 8 167 1 743 ATT TAA 2 trnH R 8 168 8 231 64 GTG 0 ND4 R 8 232 9 570 1 339 ATG T 0 ND4L R 9 602 9 895 294 ATG TAA 24 trnT F 9 900 9 964 65 TGT 7 trnP R 9 965 10 029 65 TGG 0 ND6 F 10 038 10 568 531 ATA TAA 8 CytB F 10 574 11 722 1 149 ATG TAA 4 trnS2 F 11 726 11 791 66 TGA 3 ND1 R 11 791 12 744 954 ATG TAA -1 trnL R 12 746 12 813 68 TAG 1 rrnL R 12 840 14 278 1 439 0 trnV R 14 284 14 349 66 TAC 0 rrnS R 14 350 15 122 773 0 AT region F 15 123 15 443 321 0 基因间隔一列中,正数表示基因间隔碱基数,负数表示基因重叠碱基数。
In the column of intergenic length, the positive number indicates interval base pairs between genes, while the negative indicates the overlapping base pairs between genes.表 3 云南松毛虫线粒体基因组核苷酸组成
Table 3. Nucleotide composition of the complete mitochondrial genome of Dendrolimus houi
基因序列
GenesequenceSize/bp A/% T/% C/% G/% A+T/% C+G/% 全基因组
Whole genome15 443 41.2 38.8 12.4 7.6 80.0 20.0 蛋白编码基因 PCGs 11 213 33.9 44.4 10.6 11.1 78.3 21.7 rRNA 基因 1 439 40.4 44.1 4.4 11.1 84.5 15.5 tRNA 基因 773 44.1 41.5 4.6 9.8 85.6 14.4 A+T 富集区 321 40.8 51.4 5.0 2.8 92.2 7.8 -
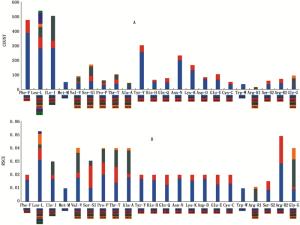
云南松毛虫线粒体基因组共编码13个蛋白质基因(COX1,COX2,COX3,ATP6,ATP8,ND1,ND2,ND3,ND4,ND4L,ND5,ND6,Cyt B)。除了COX1以CGA为起始密码子,其余均以ATN作为起始密码子。9个蛋白编码基因共享相同的终止密码子TAA(ND2,ATP8,ATP6,COX3,ND5,ND4L,ND6,CYTB和ND1),其他4个基因的终止密码子都是残缺的,COX1、COX2、ND4以T为终止密码子,ND3以TA为终止密码子。这种不完整的终止密码子在鳞翅目线粒体基因组中是很常见的,有研究推测它们会在转录后的多腺苷酸化过程中变成完整体[16]。云南松毛虫线粒体基因组的全部蛋白质编码基因的氨基酸使用情况(图 2:A)和相对密码子使用率RSCU(图 2:B)的分析结果显示,云南松毛虫13个蛋白质编码基因中氨基酸使用最频繁的依次包括Phe、Ile、Leu和Tyr(Count>300),而Ala、Met和Trp的使用相对较少(Count<50);相对同义密码子中UUA使用频率最高,RSCU值为3.12,密码子CGC和CCG的相对密码子使用频率最低,其RSCU值分别为0和0.07。
-
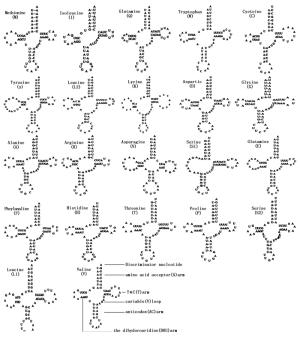
云南松毛虫线粒体基因组上共检测出22个tRNA基因,A+T的含量为81.3%,总长为1 475 bp,长度范围为64~71 bp,在线粒体基因组上的排列顺序与其它松毛虫属昆虫相同。其中14个编码在J链上(majorcoding strand),8个编码在N链上(minorcoding strand)。所有的tRNA都有经典的三叶草二级结构(图 3),除了trns1(AGN)基因,它的二氢尿苷臂(DHU)被未配对的核苷酸取代,无法形成典型的三叶草结构。在云南松毛虫线粒体基因组的22个trna基因的二级结构中出现了22对碱基错配现象。其中G-U错配20个,U-C和U-U错配各1个。U-C错配出现在tRNAThr(TGT)的TΨC臂上,U-U错配位于tRNALeu(TAA)的氨基酸接受臂上。20个G-U错配在氨基酸接受臂、TΨC臂、二氢尿嘧啶臂和反密码子臂上均有出现。这种错配普遍存在于鳞翅目昆虫的tRNA二级结构中[18]。这些错配是符合摆动配对原则的,对维持tRNA二级结构的稳定起着重要的作用。
rRNA基因是一类相对分子量较大的RNA基因,可与蛋白质结合形成核糖体。云南松毛虫线粒体的核糖体小亚基rrnS基因和核糖体大亚基rrnL基因的长度分别是773 bp和1 439 bp,分别位于A+T富含区与trna-Val(TAC)之间和trna-Val(TAC)和trna-Leu(TAG)之间。rrnS基因和rrnL基因的A+T含量为84.9%(表 3),具有明显AT碱基偏向性。
-
A + T富含区为线粒体基因组中的非编码序列,即为不能转录为相应的mRNA,从而不能指导合成相应蛋白质的区域。云南松毛虫线粒体基因组的A + T富含区位于rrnS基因与trna-Met基因之间,其长度为321 bp,A+T含量为92.2%。rrnS基因下游有一段由“ATAGA”引导的长度为14 bp的多聚T结构(图 4),这段多聚T结构在所有已测定的鳞翅目昆虫mtDNA中都很保守,长度从12 bp(宽尾凤蝶 Agehana maraho )到22 bp(野桑蚕 Bombyx mandarina )不等。在云南松毛虫线粒体A+T富含区中还存在一个(AT)7结构,这在其他鳞翅目昆虫中均有检测到类似结构[13-14]。
-
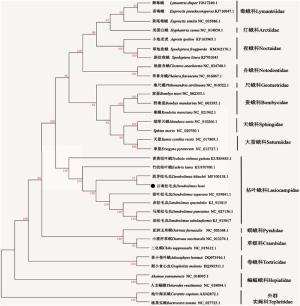
以双翅目Diptera实蝇科Tephritidae地中海实蝇 Ceratitis capitata 和桃果实蝇 Bactrocera zonata 为外群,选用已测定的13个科的鳞翅目蛾类昆虫和本研究中的云南松毛虫线粒体全基因组,基于13个蛋白编码基因的核苷酸序列构建ML树。结果显示(图 5),枯叶蛾科中云南松毛虫与其他物种的系统发育关系为:((((((马尾松毛虫+油松毛虫)+赤松毛虫)+落叶松毛虫)+(思茅松毛虫+云南松毛虫))+竹纹枯叶蛾)+青黄枯叶蛾)。13种鳞翅目昆虫的系统发育分析结果显示,枯叶蛾科Lasiocampidae与蚕蛾科Bombycidae、大蚕蛾科Satumiidae、天蛾科Sphingidae和尺蛾科Geometriidae聚为一簇,并且有很高的支持率;来自夜蛾总科的舟蛾科Notodontidae,夜蛾科Noctuidae,灯蛾科Hypercompe和毒蛾科Lymantriidae聚为一簇,系统发育关系为:((毒蛾科+灯蛾科)+夜蛾科+舟蛾科);螟蛾总科的螟蛾科Pyralidae与草螟科Cramnidae聚为一簇;卷蛾科Tortricidae和蝙蝠蛾科Hepialidae单独聚类。
-
松毛虫属内系统发育结果显示(图 6),松毛虫属几个近缘种以较高的支持率分为两支。系统发育关系为:(((((油松毛虫+文山松毛虫)+赤松毛虫)+落叶松毛虫)+(思茅松毛虫+云南松毛虫))+家蚕)。基于K2P模型计算松毛虫属内种间的遗传距离(表 4),结果显示:思茅松毛虫与其他松毛虫的遗传距离最大。马尾松毛虫、文山松毛虫、赤松松毛虫、油松毛虫与云南松毛虫间的遗传距离略小于思茅松毛虫与云南松毛虫的遗传距离;油松毛虫与马尾松毛虫间的遗传距离(0.011 8)小于文山松毛虫与马尾松毛虫间(0.013 5)的遗传距离,三者与赤松毛虫间的遗传距离均较大,表明赤松毛虫与三者亲缘关系较远。

图 6 基于松毛虫属13个蛋白编码基因的NJ系统发育树
Figure 6. NJ phylogenetic tree based on 13 protein-coding genes of Dendrolimus
表 4 松毛虫属间的K2P遗传距离
Table 4. K2P genetic distance between species of the Dendrolimus
种群代码
population codeD.pun D.pun ws D.tab D.spet D.sup D.kiku D.houi Bombyx mori D.pun D.pun ws 0.013 5 D.tab 0.011 8 0.007 1 D.spet 0.051 2 0.052 2 0.051 8 D.sup 0.070 6 0.072 7 0.071 9 0.071 0 D.kiku 0.098 2 0.100 3 0.098 9 0.100 4 0.097 5 D.houi 0.092 5 0.095 3 0.093 4 0.091 2 0.086 8 0.094 2 Bombyx mori 0.193 6 0.195 6 0.194 5 0.193 5 0.191 7 0.198 5 0.189 4 -
云南松毛虫线粒体基因组全长15 443 bp,A+T含量为80.0%,基因组的排列同已报道的鳞翅目其他昆虫的线粒体基因排列一致[17-18]。其中trnM-trnI-trnQ的排列方式与假想昆虫祖先的排列方式(trnI-trnQ-trnM)不同[19],但是这种排列在鳞翅目昆虫中非常典型。鳞翅目线粒体基因组进化上的保守性,表明其适合解决科、目等高级阶元的系统发育问题[20]。
松毛虫属内系统发育树图显示,云南松毛虫和思茅松毛虫有共同祖先,而思茅松毛虫较早的与云南松毛虫分化,二者独立进化。有研究表明,二者的触角转录组表现出高度相似性,证明它们有很近的亲缘关系。从信息素角度出发,思茅松毛虫性信息素成分包括Z5,E7-12:OAc、Z5,E7-12:OH和Z5-12:OAc 3种成分[21],而云南松毛虫性信息素成分包括E5,Z7-12:OH和E5,Z7-12:OAc[22],不同的性信息素成分使它们产生了生殖隔离。马-文-油-赤拥有共同祖先,且分化的时间较晚。云南松毛虫与思茅松毛虫的共同祖先种群与落-赤-马-油-文5种松毛虫的共同祖先互为姊妹群,拥有更高级的共同祖先。从松毛虫的分化情况来看,云南松毛虫应该是松毛虫属的基础物种,与其他松毛虫物种亲缘关系较远,这与Alexander Kononov等人[23]基于线粒体 COI 、 COII 和核基因ITS2的研究结果一致,遗传距离结果也显示云南松毛虫与其他松毛虫之间存在较大的遗传距离。遗传距离结果中油松毛虫×文山松毛虫的遗传距离(0.007 1)<油松毛虫×马尾松毛虫间的遗传距离(0.011 8)<文山松毛虫×马尾松毛虫间(0.013 5)的遗传距离,而文山松毛虫是马尾松毛虫公认的地理亚种[10],这也支持油松毛虫和文山松毛虫作为马尾松毛虫地理亚种的分类地位。
鳞翅目蛾类高级分类阶元系统发育结果显示,枯叶蛾科与蚕蛾总科、尺蛾总科和夜蛾总科聚为一支,其系统发育关系为:(枯叶蛾科+(夜蛾总科+(尺蛾总科+蚕蛾总科))),这与Qin等人[10]报道的枯叶蛾科、蚕蛾总科和尺蛾总科的系统发育关系:(((天蛾科+蚕蛾科)+大蚕蛾科+尺蛾科)+枯叶蛾科)相一致。夜蛾总科中的舟蛾科、夜蛾科、毒蛾科和灯蛾科的进化关系为:((舟蛾科+(夜蛾科+(毒蛾科+灯蛾科))),舟蛾科、夜蛾科和毒蛾科的进化关系和吴榴宇[24]得到的科级阶元系统发育结果:((裳蛾科+毒蛾科)+夜蛾科)+舟蛾科相一致。由此可见鳞翅目蛾类几大总科之间的系统发育关系较稳定,该结果在多数研究中均被验证[25-26]。本研究通过测定云南松毛虫线粒体全基因组序列,分析其碱基组成、结构特点及其在高级阶元下与其他物种间的系统发育关系,丰富了枯叶蛾科线粒体基因组数据库,为枯叶蛾科物种鉴定、分类和进化分析奠定了分子基础。
-
测定和分析了云南松毛虫线粒体基因组特征,全长15 443 bp,包括13个蛋白质编码基因,22个tRNA基因,2个rRNA基因和一段长度为321bp的A+T富含区,无基因重排,存在较高的A+T含量(80.0%)。整个线粒体结构与鳞翅目中目前已得到的其他昆虫线粒体基因组结构一致。获得了松毛虫属内近源种间系统发育关系:(((((油松毛虫+文山松毛虫)+赤松毛虫)+落叶松毛虫)+(思茅松毛虫+云南松毛虫))+家蚕);鳞翅目蛾类各科之间的系统发育关系:((((((((毒蛾科+灯蛾科)+夜蛾科)+舟蛾科)+(尺蛾科+(蚕蛾科+(天蛾科+大蚕蛾科))))+枯叶蛾科)+(螟蛾科+草螟科))+卷蛾科)+蝙蝠蛾科)。
云南松毛虫线粒体基因组全序列测定和分析
Sequencing and Analysis of Complete Mitochondrial Genome of Dendrolimus houi Lajonquiere (Lepidoptera: Lasiocampidae)
-
摘要:
目的 测定和分析了云南松毛虫线粒体基因组特征,从线粒体基因组水平探究鳞翅目蛾类昆虫高级阶元的系统发育关系。 方法 采用Illumina HiSeq测序方法测定了云南松毛虫线粒体全基因组序列,参考鳞翅目昆虫已知线粒体基因组的全序列对其各基因进行定位和注释。采用tRNA Scan-SE 2.0在线预测云南松毛虫线粒体基因组tRNA基因的二级结构。基于线粒体全基因组的蛋白编码序列构建了鳞翅目13个科32种蛾类昆虫的系统发育树和松毛虫属近缘种间的系统发育树。 结果 结果显示云南松毛虫线粒体基因组全长15 443 bp,包括13个蛋白质编码基因,22个tRNA基因,2个rRNA基因和一段长度为321 bp的A+T富含区,无基因重排,存在较高的A+T含量(80.0%)。13个蛋白编码基因中除了 ND2和 COX1,其余均以ATN做为起始密码子。9个蛋白编码基因共享相同的终止密码子TAA( ND2、 ATP8、 ATP6、 COX3、 ND5、 ND4L、ND6、CYTB和 ND1),其他4个基因的终止密码子都是残缺的, COX1、 COX2、 ND4以T为终止密码子, ND3以TA为终止密码子。22个tRNA基因中,除了tRNASer(AGN)由于缺少DHU臂无法构成三叶草结构,其余T均为典型的三叶草结构。整个线粒体结构与鳞翅目中目前已得到的其他昆虫线粒体基因组结构一致。 结论 系统发育分析结果显示,云南松毛虫与思茅松毛虫是完全不同的近缘种,与其他松毛虫亲缘关系也较远,云南松毛虫与6种近缘种的系统发育关系为:(((((油松毛虫+文山松毛虫)+赤松毛虫)+落叶松毛虫)+(思茅松毛虫+云南松毛虫))+家蚕)。鳞翅目蛾类各科之间的系统发育关系为:((((((((毒蛾科+灯蛾科)+夜蛾科)+舟蛾科)+(尺蛾科+(蚕蛾科+(天蛾科+大蚕蛾科))))+枯叶蛾科)+(螟蛾科+草螟科))+卷蛾科)+蝙蝠蛾科)。 Abstract:Objective To identify and analyze the mitochondrial genome of Dendrolimus houi Lajonquiere, and to study the higher-level phylogenetic relationship of Lepidoptera moths based on the mitochondrial genome. Method The Illumina Hiseq technique was chosen to sequence the purified mitochondrial DNA of D. houi . The genes were located and annotated based on the known complete mitochondrial genomes of Lepidopteran species. The tRNA Scan-SE 2.0 was used to predict the secondary structure of the tRNA genes online. Based on the PCGs of the whole nucleotide sequences of mitochondrial genome, the phylogenetic trees of 32 species from 12 families of Lepidoptera moths and the phylogenetic trees of the relative species of the Dendrolimus were reconstructed. Result The results indicated that the complete mitochondrial genome of D. houi is 15 443 bp in length, including 13 protein-coding genes (PCGs), 22 tRNA genes, 2 rRNA genes and a 321 bp A+T-rich region, without gene rearrangement, and showed a higher A+T content (80.0%). All these PCGS except for ND2 and COX1, used ATN as the start codon. Nine PCGs shared the same stop codon TAA, and the stop codons of the other four genes were all defective. COX1, COX2, and ND4 used T as the stop codon and ND3 used TA as the stop codon. Among the 22 tRNA genes, tRNASer (AGN) lacked the DHU arm and could not form a clover structure, while the remaining tRNAs were typical clover structures. The mitochondrial structure was consistent with other insect's mitochondrial genome structures currently available in Lepidoptera. Conclusion The phylogenetic analysis indicates that D. houi and D. kikuchii are completely different relatives, and the relationship between D. houi and other Dendrolimus species is also far away. The phylogenetic relationship is:((((( D. tabulaeformis + D. punctatus wenshanensis ) + D. spectabilis + D. superans ) + ( D. houi + D. kikuchii )) + Bombyx mori ). The phylogenetic relationship between the families of Lepidoptera is:((((((((Lymantriidae + Arctiidae) + Noctuidae) + Notodontidae) + (Geometriidae + (Bombycidae + (Sphingidae + Satumiidae)))) + Lasiocampidae) + (Pyralidae + Cramnidae)) + Tortricidae) + Hepialidae). -
Key words:
- Lepidoptera
- / Lasiocampidae
- / Dendrolimus houi
- / mitochondrial genome
- / phylogeny
-
表 1 用于高级阶元系统发育分析的物种信息
Table 1. Information of species used for phylogenetic analysis
科名 Family 物种 Species 线粒体基因组大小
mt DNA Size/bp(A+T)/% GenBank登录号
GenBank accession no.枯叶蛾科 Lasiocampidae 云南松毛虫 Dendrolimus houi 15 443 80.0 - 马尾松毛虫 Dendrolimus punctatus 15 417 79.5 NC_027156.1 思茅松毛虫 Dendrolimus kikuchii 15 422 79.2 MF100138.1 油松毛虫 Dendrolimus tabulaeformis 15 411 79.5 KJ_913817 赤松毛虫 Dendrolimus spectabilis 15 412 79.3 KJ_913815 落叶松毛虫 Dendrolimus superans 15 417 80.1 NC_039841.1 竹纹枯叶蛾 Euthrix laeta 15 368 80.2 KU870700.1 青黄枯叶蛾 Trabala vishnou guttata 15 281 80.9 KU884483.1 天蛾科 Sphingidae 烟草天蛾 Manduca sexta 15 516 81.8 NC_010266.1 Sphinx morio 15 299 81.1 NC_020780.1 大蚕蛾科 Saturniidae 天蚕 Samia cynthia ricini 15 384 79.7 NC_017869.1 章蚕 Eriogyna pyretorum 15 327 80.8 NC_012727.1 夜蛾科 Noctuidae 小地老虎 Agrotis ipsilon 15 377 81.3 KF163965.1 草地夜蛾 Spodoptera frugiperda 15 365 81.1 KM362176.1 斜纹夜蛾 Spodoptera litura 15 383 81.1 KF701043 毒蛾科 Lymantriidae 舞毒蛾 Lymantria dispar 15 569 79.9 FJ617240.1 黄尾毒蛾 Euproctis similis 15 437 80.2 NC_035886.1 茶毒蛾 Euproctis pseudoconspersa 15 461 79.7 KJ716847.1 尺蛾科 Geometridae 桑尺蠖 Phthonandria atrilineata 15 499 81.0 NC_010522.1 蝙蝠蛾科 Hepialidae Ahamus yunnanensis 15 816 82.3 NC_018095.1 人支蝠蛾 Thitarodes renzhiensis 16 173 81.3 NC_018094.1 蚕蛾科 Bombycidae 桑蟥 Rondotia menciana 15 306 78.8 NC_021962.1 家蚕 Bombyx mori 15 643 81.3 NC_002355.1 野桑蚕 Bombyx mandarina 15 928 81.7 NC_003395.1 灯蛾科 Arctiidae 美国白蛾 Hyphantria cunea 15 481 80.4 NC_014058.1 螟蛾科 Pyralidae 亚洲玉米螟 Ostrinia furnacalis 14 563 80.4 NC_003368.1 舟蛾科 Notodontidae 苹掌舟蛾 Phalera flavescens 15 659 80.9 NC_016067.1 杨扇舟蛾 Clostera anachoreta 15 456 80.7 NC_034740.1 草螟科 Crambidae 小蔗杆草螟 Diatraea saccharalis 15 490 80.1 NC_013274.1 二化螟 Chilo suppressalis 15 395 80.6 NC_015612.1 卷蛾科 Tortricidae 茶小卷叶蛾 Adoxophyes honmai 15 680 80.4 DQ073916.1 梨小食心虫 Grapholita molesta 15 717 80.9 HQ392511.1 双翅目 Diptera 地中海实蝇 Ceratitis capitata 15 980 77.5 AJ242872.1 实蝇科 Tephritidae 桃果实蝇 Bactrocera zonata 15 935 73.4 NC_027725.1 表 2 云南松毛虫线粒体基因组注释
Table 2. Organization of the mitochondrial genome of Dendrolimus houi
基因
Gene方向
Direction位置
Location长度
Size反密码子
Anticodon起始密码子
Startcodon终止密码子
Stop codon基因间隔
IntergenictrnM F 1 67 67 CAT trnI F 69 132 64 GAT 7 trnQ R 130 198 69 TTG -1 ND2 F 257 1 264 1 008 TTT TAA 58 trnW F 1 263 1 332 70 TCA -2 trnC R 1 325 1 391 67 GCA -8 trnY R 1 393 1 463 71 GTA 0 COX1 F 1 492 3 022 1 531 CGA T 34 trnL F 3 023 3 089 67 TAA 0 COX2 F 3 090 3 771 682 ATA T 0 trnK F 3 775 3 845 71 CTT 0 trnD F 3 847 3 913 67 GTC 3 ATP8 F 3 914 4 075 162 ATT TAA 0 ATP6 F 4 069 4 746 678 ATG TAA -7 COX3 F 4 762 5 550 789 ATG TAA 14 trnG F 5 553 5 618 66 TCC 2 ND3 F 5 619 5 971 353 ATT TA 0 trnA F 5 971 6 038 68 TGC -1 trnR F 6 048 6 112 65 TCG 15 trnN F 6 118 6 184 67 GTT 4 trnS1 F 6 211 6 276 66 GCT 11 trnE F 6 277 6 345 69 TTC -1 trnF R 6 354 6 420 67 GAA 4 ND5 R 6 425 8 167 1 743 ATT TAA 2 trnH R 8 168 8 231 64 GTG 0 ND4 R 8 232 9 570 1 339 ATG T 0 ND4L R 9 602 9 895 294 ATG TAA 24 trnT F 9 900 9 964 65 TGT 7 trnP R 9 965 10 029 65 TGG 0 ND6 F 10 038 10 568 531 ATA TAA 8 CytB F 10 574 11 722 1 149 ATG TAA 4 trnS2 F 11 726 11 791 66 TGA 3 ND1 R 11 791 12 744 954 ATG TAA -1 trnL R 12 746 12 813 68 TAG 1 rrnL R 12 840 14 278 1 439 0 trnV R 14 284 14 349 66 TAC 0 rrnS R 14 350 15 122 773 0 AT region F 15 123 15 443 321 0 基因间隔一列中,正数表示基因间隔碱基数,负数表示基因重叠碱基数。
In the column of intergenic length, the positive number indicates interval base pairs between genes, while the negative indicates the overlapping base pairs between genes.表 3 云南松毛虫线粒体基因组核苷酸组成
Table 3. Nucleotide composition of the complete mitochondrial genome of Dendrolimus houi
基因序列
GenesequenceSize/bp A/% T/% C/% G/% A+T/% C+G/% 全基因组
Whole genome15 443 41.2 38.8 12.4 7.6 80.0 20.0 蛋白编码基因 PCGs 11 213 33.9 44.4 10.6 11.1 78.3 21.7 rRNA 基因 1 439 40.4 44.1 4.4 11.1 84.5 15.5 tRNA 基因 773 44.1 41.5 4.6 9.8 85.6 14.4 A+T 富集区 321 40.8 51.4 5.0 2.8 92.2 7.8 表 4 松毛虫属间的K2P遗传距离
Table 4. K2P genetic distance between species of the Dendrolimus
种群代码
population codeD.pun D.pun ws D.tab D.spet D.sup D.kiku D.houi Bombyx mori D.pun D.pun ws 0.013 5 D.tab 0.011 8 0.007 1 D.spet 0.051 2 0.052 2 0.051 8 D.sup 0.070 6 0.072 7 0.071 9 0.071 0 D.kiku 0.098 2 0.100 3 0.098 9 0.100 4 0.097 5 D.houi 0.092 5 0.095 3 0.093 4 0.091 2 0.086 8 0.094 2 Bombyx mori 0.193 6 0.195 6 0.194 5 0.193 5 0.191 7 0.198 5 0.189 4 -
[1] 侯陶谦.中国松毛虫[M].北京:科学出版社, 1987.6-31. [2] 陈昌洁.松毛虫综合管理[M].北京:中国林业出版社, 1990.5-25. [3] Kong X B, Zhang Z, Zhao C H, et al . Female Sex Pheromone of the Yunnan Pine Caterpillar Moth Dendrolimus houi :First (E, Z)-Isomers in Pheromone Components of Dendrolimus spp[J]. Journal of Chemical Ecology, 2007, 33(7):1316-1327. doi: 10.1007/s10886-007-9313-2 [4] 张爱兵, 孔祥波, 李典谟, 等.中国松毛虫属八个种和亚种亲缘关系的DNA指纹证据[J].昆虫学报, 2004(2):236-242. doi: 10.3321/j.issn:0454-6296.2004.02.017 [5] 南宫自艳, 高宝嘉, 杨君.松毛虫属( Dendrolimus )部分种类亲缘关系与遗传分化的等位酶分析[J].生态学报, 2009, 29(4):1661-1667. doi: 10.3321/j.issn:1000-0933.2009.04.003 [6] 南宫自艳, 杨君, 徐秀平, 等.四种松毛虫不同地理种群遗传多样性的等位酶分析[J].昆虫学报, 2008(4):417-423. doi: 10.3321/j.issn:0454-6296.2008.04.011 [7] 南宫自艳, 高宝嘉, 徐志娥, 等.松毛虫属5种松毛虫不同地理种群RAPD遗传多样性分析[J].农业生物技术学报, 2009, 17(1):178-179. doi: 10.3969/j.issn.1674-7968.2009.01.031 [8] 高宝嘉, 高立杰, 侯建华, 等.三种松毛虫不同地理种群遗传多样性[J].生态学报, 2008(2):842-848. doi: 10.3321/j.issn:1000-0933.2008.02.048 [9] 贾玉迪, 孔祥波, 张真, 等.基于线粒体 COI 基因部分序列分析4种松毛虫的亲缘关系[J].东北林业大学学报, 2011, 39(11):67-70+78. doi: 10.3969/j.issn.1000-5382.2011.11.019 [10] Qin J, Zhang Y Z, Kong X B, et al . Mitochondrial phylogenomics and genetic relationship of closely related pine moth (Lasiocampidae: Dendrolimus ) species in China, using whole mitochondrial genomes[J]. BMC Genomics, 2015, 16(1):428-439. [11] 张亚平, 施立明.动物线粒体DNA多态性的研究概况[J].动物学研究, 1992(3):289-298. [12] Brown W M, George M, Wilson A C. Rapid evolution of animal mitochondrial DNA[J]. Proceedings of the National Academy of Sciences, 1979, 76(4):1967-1971. doi: 10.1073/pnas.76.4.1967 [13] Kong W, Yang J. The complete mitochondrial genome of Rondotia menciana (Lepidoptera:Bombycidae)[J]. Journal of Insect Science, 2015, 15(1):48-48. doi: 10.1093/jisesa/iev032 [14] 张敏, 赵盼, 尹洁, 等.小红珠绢蝶线粒体基因组特征及基于线粒体基因组的蝶类高级阶元系统发育关系分析[J].昆虫学报, 2017, 60(11):1324-1338. [15] Kumar S, Stecher G, Tamura K. MEGA7:Molecular Evolutionary Genetics Analysis version 7.0 for bigger datasets[J]. Molecular Biology & Evolution, 2016, 33(7):1870. [16] Ojala D, Montoya J, Attardi G. tRNA punctuation model of RNA processing in human mitochondria[J]. Nature, 1981, 290(5806):470-474. doi: 10.1038/290470a0 [17] Liu J H, Fu J Q, Yang L Y, et al . Complete mitochondrial genome of Simao pine caterpillar moth, Dendrolimus kikuchii (Lepidoptera:Lasiocampidae) and the related phylogenetic analysis[J]. Mitochondrial DNA Part B:Resources, 2017, 2(2), 611-612. doi: 10.1080/23802359.2017.1372725 [18] 王菊平, 曹天文, 张越, 等.扬眉线蛱蝶线粒体基因组全序列测定和分析[J].昆虫学报, 2017, 60(8):950-961. [19] Boore J L, Lavrov D V, Brown W M. Gene translocation links insects and crustaceans[J]. Nature, 1998, 392(6677):667-668. doi: 10.1038/33577 [20] Boore J L. Animal mitochondrial genomes[J]. Nucleic Acids Research, 1999, 27(8):1767-1780. doi: 10.1093/nar/27.8.1767 [21] Kononov A, Ustyantsev K, Wang B, et al . Genetic diversity among eight Dendrolimus species in Eurasia (Lepidoptera:Lasiocampidae) inferred from mitochondrial COI and COⅡ, and nuclear ITS2 markers[J]. BMC Genetics, 2016, 17(3 Supplement). [22] 孙付存, 孔祥波, 张苏芳, 等.思茅松毛虫3个地理种群性信息素成分差异分析[J].林业科学研究, 2017, 30(6):993-998. [23] Kong X B, Zhang Z, et al . Female sex pheromone of the Yunnan pine caterpillar moth Dendrolimus houi :first (E, Z)-Isomers in pheromone components of Dendrolimus spp[J]. Journal of Chemical Ecology, 2007, 33(7):1316-1327. doi: 10.1007/s10886-007-9313-2 [24] 吴榴宇.竹纹枯叶蛾和青黄枯叶蛾线粒体基因组特征及系统发育研究[D].南昌: 南昌大学, 2017. [25] 王维, 孟智启, 石放雄, 等.鳞翅目昆虫比较线粒体基因组学研究进展[J].科学通报, 2013, 58(30):3017-3029. [26] Kong W, Yang J. The complete mitochondrial genome of Rondotia menciana (Lepidoptera:Bombycidae)[J]. Journal of Insect Science, 2015, 15(1):48-48. doi: 10.1093/jisesa/iev032 -



 下载:
下载: