-
油菜素内酯(BR)是一类甾醇类植物激素,在很低的浓度下即可表现出很强的生理生化效应[1],能参与调控植物生长发育和逆境胁迫等许多重要的生理过程[2]。BRI1(brassinosteroid insensitive 1)作为BR的受体,在BR信号转导中起重要作用。BRI1属于富含亮氨酸重复类受体激酶(LRR-RLK),其结构主要由胞外区、跨膜区和胞内激酶区3部分组成[3],其中,胞外区包括1个亮氨酸拉链基序,1个N端信号肽,25个富含亮氨酸重复单位( LRR)以及在第21和第22个LRR之间有一个由70个氨基酸组成的ID(island domain)结构[4-5],该结构是BR的识别区域[6];而BRI1-like3(BRI1-like receptor genes 3)作为BRI1蛋白家族成员,也参与了BR信号识别转导过程[7-8]。
研究发现,BRI1在植物花发育上有着重要的作用,Nie等在番茄(Solanum lycopersicum L.)中过表达了SlBRI1基因,结果发现番茄花变大且花瓣和花柱变长[9];Singh等发现,小麦(Triticum aestivum L.)TaBRI1基因在拟南芥(Arabidopsis thaliana L.)中过表达会导致转基因拟南芥提前开花[10];雷世康等发现,麻疯树(Jatropha curcas L.)油菜素内酯受体基因JcBRI1介导的BR途径可能对麻疯树雌花发育有一定的促进作用[11]。然而,目前关于BRL3参与花发育方面的研究还未见报道。
麻疯树果实含油率高达60%,是最具潜力的生物柴油原料树种[12]。然而,由于麻疯树结实少、种子产量低等原因严重阻碍了其大规模种植和发展,而雌雄花比例低(约为1/30~1/10)是导致麻疯树结实少的重要原因之一[13]。本研究从麻疯树花蕾转录组数据中筛选到了一个性别差异表达的油菜素内酯受体蛋白基因BRI1-like3(BRL3),利用RACE PCR技术获得了JcBRL3基因的全长cDNA;通过LC-MS/MS技术鉴定了JcBRL3的原核表达产物(蛋白质);通过在线软件对JcBRL3蛋白的结构进行了生物信息学分析;通过qRT-PCR技术分析了该基因在麻疯树花发育过程中的表达模式,并通过该基因的转基因烟草对其功能进行了初步验证。
-
本研究材料为贵州省黔西南州贞丰县采集而来麻疯树花蕾,收集完花蕾样品后将其放进非冻型组织RNA保护液中。将不同时期的麻疯树花蕾在4℃平衡48 h后分成9类,分别为性别未分化时期、雌花大孢子母细胞时期、雌花大孢子母细胞分裂期、雌花单核胚囊期、雌花胚囊成熟期、雄花小孢子母细胞时期、雄花四分体时期、雄花单核花粉粒时期以及雄花花粉粒成熟期[11],随后放入−80℃超低温冰箱中保存备用。
-
麻疯树总RNA的提取参照Plant RNA Kit(OMEGA)说明书进行。采用SMARTer® RACE 5′/3′ Kit(Clontech)试剂盒进行5′/3′ RACE扩增,引物见表1。PCR产物用NuceloSpin Gel and PCR Clean-Up Kit(TaKaRa)胶回收纯化后与pUC19载体连接,利用In-Fusion® HD Cloning Kit(TaKaRa)进行转化,筛选阳性克隆于生工生物工程股份有限公司(上海)测序验证。将测序成功的5′cDNA片段、3′cDNA片段和已知中间片段通过DNAMAN软件拼接,从而获得JcBRL3基因全长cDNA序列。
表 1 本研究所用引物及其序列
Table 1. Primers sequences and ways of use in this study
引物
Primers引物序列
Sequence(5′→3′)引物用途
Usage3′GSP GATTACGCCAAGCTTGGCTTCTTCCAGTAATGATGAAGTTGC 全长克隆 5′GSP GATTACGCCAAGCTTCAGTATTTGTGAGGTTGAGGGCAGTAA 全长克隆 UPM CTAATACGACTCACTATAGGGCAAGCAGTGGTATCAACGCAGAGT 全长克隆 JcBRL3-F GGAATTCCATATGCAGTAATGATGAAGTTGCGGGGTTA 原核表达载体构建 JcBRL3-R CCCAAGCTTAGAGAGATTGTTGTTAGAGACATCA 原核表达载体构建 QJcBRL3-F GCTTGACTTGAACAGCAACGACCTT 荧光定量PCR QJcBRL3-R TCCTGACACAACGCCTGGAACAAT 荧光定量PCR JcActin-F TCCCTGGTATTGCTGACCGTAT 荧光定量PCR(内参基因) JcActin-R TGGACAATGGATGGACCAGACT 荧光定量PCR(内参基因) JcTubulin-F CTCTGCAACTATGAGTGGTGTAACG 荧光定量PCR(内参基因) JcTubulin-R CACGAGAAGTAAGTGGGGCAAA 荧光定量PCR(内参基因) GMJcBRL3-F CAGTGGTCTCACAACATGAAGAAACAATGGAGAAT 过表达载体构建 GMJcBRL3-R CAGTGGTCTCATACATCATGAACTTTGAGATTCTT 过表达载体构建 JcBRL3st-F TGCCTGACCTCATCGCTGCTT 转基因烟草检测 JcBRL3st-R CCTGACACAACGCCTGGAACAA 转基因烟草检测 -
使用限制性内切酶Hind III和Nde I对目的基因ORF与原核表达载体pET-30a(+)进行双酶切,经胶回收纯化连接后转化到Escherichia coli DH5α感受态细胞中。提取阳性菌株质粒进行测序验证,将测序正确的重组载体(pET-30a-JcBRL3)分别转化到E. coli BL21(DE3)和E. coli Rosetta(DE3)感受态细胞中。挑取单克隆接种于含卡那霉素(50 μg·mL−1)的LB液体培养基中过夜培养,其中,E. coli Rosetta(DE3)中需再加入氯霉素(20 μg·mL−1)。次日以1:100的体积比接种到LB液体培养基中(抗生素与之前相同),待OD600为0.5~0.8时,向液体培养基中加入IPTG(终浓度为0.1 mmol·L−1),分别置于15℃和37℃下进行培养,培养时间均为16 h,诱导JcBRL3重组蛋白的表达,再用SDS-PAGE电泳对重组蛋白的表达进行检测。
-
将SDS-PAGE凝胶的目的条带切下装入离心管中,经脱水脱色后使用胰蛋白酶于37℃水浴过夜酶解,之后提出肽段制成冻干粉。取5 μL含0.1%TFA的溶液将干粉重新溶解,再按1:1的比例与α-氰基-4-羟基肉桂酸饱和溶液混合(含50%ACN和1%TFA),制成上样液,取1 μL样品进行质谱点靶鉴定[11]。质谱数据分析和蛋白鉴定采用Mascot 2.1(Matrix S cience)软件进行。
-
利用在线工具分别对麻疯树JcBRL3蛋白的信号肽(SignalP 4.1 Server)、跨膜结构(TMHMMServerV.2.0)、磷酸化位点(NetPhos3.1Server)、二级结构(GOR4)、三级结构(SWISS-MODEL)以及保守结构域(NCBI-CDD)进行预测和分析。利用Uniport数据库检索JcBRL3蛋白,通过Clustal X软件对与JcBRL3蛋白含相同结构域的同源蛋白进行多重比对分析。通过MEGA 6.0 软件的邻接法(Neighbor-Joining),Poissoncorrection模型,Bootstrap检验为1 000来构建系统发育树。
-
按照Plant RNA Kit(OMEGA)试剂盒说明书分别提取麻疯树花蕾9个关键发育时期的RNA,对RNA浓度和质量进行检测后,取等量RNA反转录形成cDNA。所用荧光定量PCR引物见表1。以麻疯树花蕾未分化时期为对照组,以β-Actin和Tubulin为内参基因,每个样品设置3个技术重复与3个生物重复,相对表达量采用2−ΔΔCT法计算,再利用SPSS20.0软件对数据进行单因素方差分析(One-way ANOVA)。
-
通过Golden Gate assembly技术构建JcBRL3基因ORF与载体pBWA(V)KS-ccDB的植物过表达载体。通过冻融法将pBWA(V)KS-BRL3质粒转化到根癌农杆菌LBA4404感受态细胞,涂板于含卡那霉素(50 μg·mL−1)和利福平(20 μg·mL−1)的YEP固体培养上,挑取阳性菌落测序验证。将测序正确的农杆菌菌液划线培养,挑取单菌落接种于YEP液体培养基中过夜培养,第2天取1 mL菌液加入到50 mL YEP液体培养基中,当OD600培养到0.4~0.7时,将菌液转移到离心管中,离心收集菌体。
-
用MS重悬液重悬农杆菌,再通过叶盘转化法将目的基因转入烟草K326,之后置于培养基中培养到烟草幼苗形成,再对其进行移植。分别提取野生型烟草和转基因烟草的DNA与RNA,进行PCR与RT-PCR检测,判断目的基因是否整合至烟草抗性植株基因组中以及能否在烟草体内转录成功,检测所用引物见表1。
-
采集2株野生型及3株转基因烟草处于散粉期的花药,每株3个(共15个),经戊二醛和锇酸双重固定、脱水干燥、对花粉粒喷金处理后于扫描电镜(SU8100)下观察拍照并计算花粉粒畸形率。
-
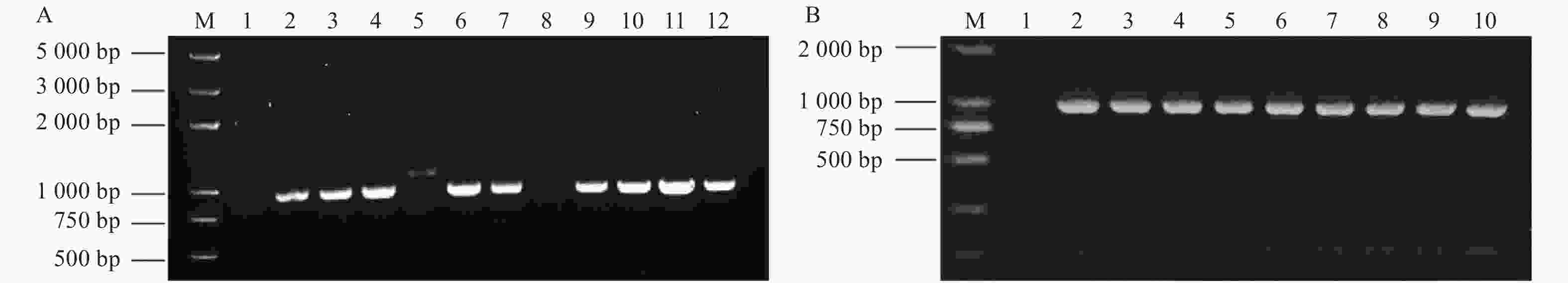
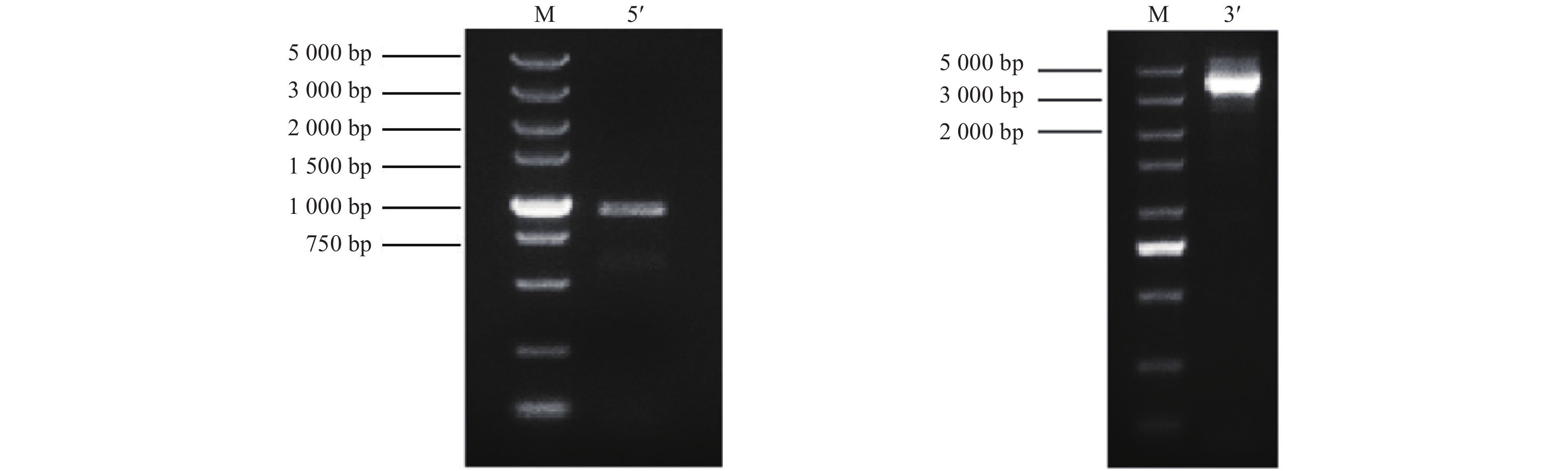
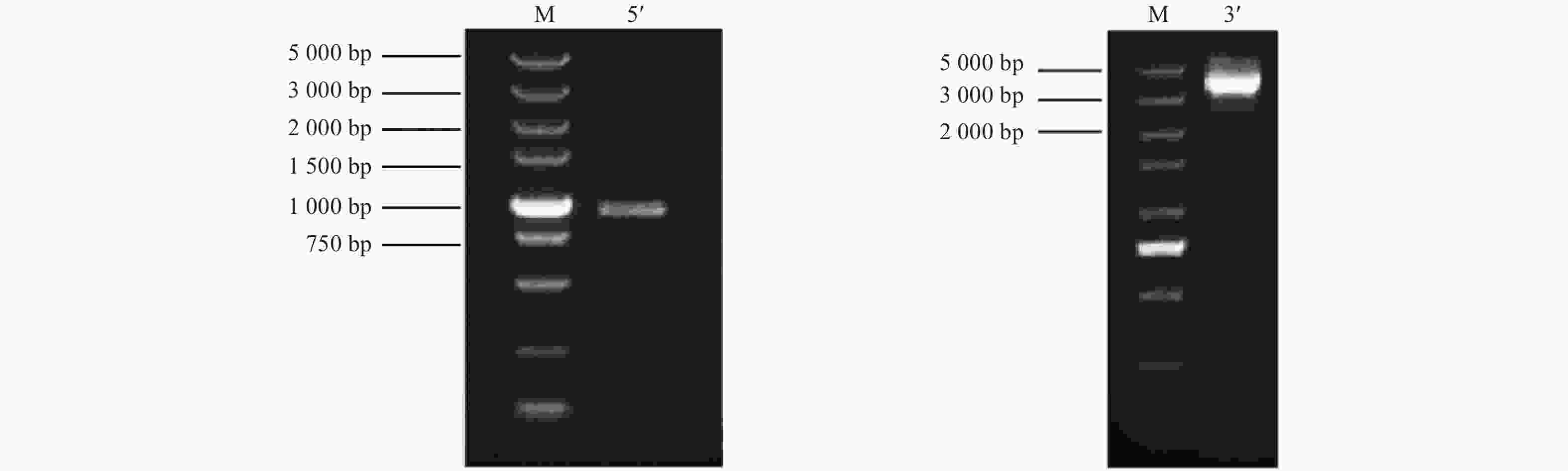
利用RACE PCR技术获得JcBRL3基因的5'RACE和3'RACE片段(图1),经拼接得到cDNA全长4 755 bp,该基因的开放阅读框(ORF)为3 618 bp,编码1 205个氨基酸,分子量为130.71 kDa,等电点(pI)为6.06(GenBank登录号:MG879232)
-
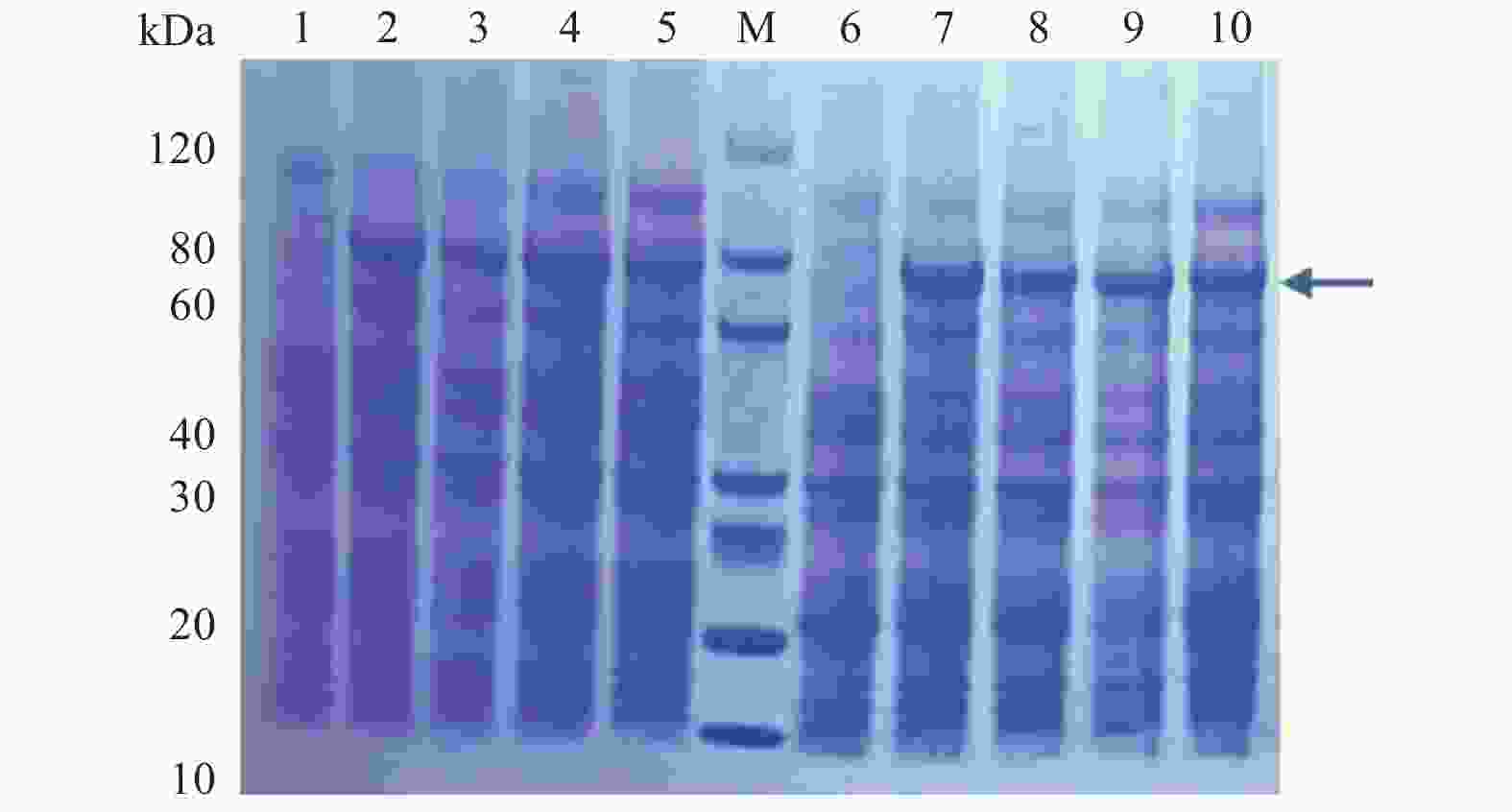
将构建好的原核表达载体pET-30a(+)-JcBRL3转化到E. coli BL21(DE3)与E. coli Rosetta(DE3)感受态细胞中,在15℃与37℃温度下诱导16 h后,离心收集菌体进行SDS-PAGE分析。结果表明:JcBRL3蛋白大约在80 kDa左右出现目的条带,与预测的蛋白理论分子量几乎一致,说明JcBRL3基因在E. coli BL21(DE3)与E. coli Rosetta(DE3)中均可成功表达,且在相同的诱导时间,15℃与37℃不同的诱导温度下,JcBRL3蛋白有同样的表达情况(图2)。
-
质谱鉴定结果表明:JcBRL3在原核表达系统得到表达,共有16条特异的肽段与JcBRL3蛋白(A0A067KCE7)氨基酸序列相匹配(表2),序列覆盖率达到了100%,蛋白分子量为84.7 kDa,蛋白得分为615,这表明JcBRL3基因的表达产物就是JcBRL3蛋白(A0A067KCE7)。
表 2 16条匹配肽段
Table 2. 16 matched peptide segments
编号
Number肽段
Sequence分子量
Molecular weight/Da误差
Error(± Da)起始序列
Start sequence终止序列
Terminator sequence估算值
Estimated value观测值
Observed value1 NEGGTSCR 880.357 7 880.379 8 0.022 1 613 620 2 GAGGLVEFEGIR 1 204.632 1 1 204.646 0 0.013 9 621 632 3 FCTSSNPSALQK 1 339.631 1 1 339.645 9 0.014 8 419 430 4 FSGNLETIPLSCK 1 465.735 6 1 465.740 8 0.005 2 187 199 5 FSGNLETIPLSCKR 1 621.836 7 1 621.854 5 0.017 8 187 200 6 LENFPMVHSCPTTR 1 688.788 3 1 688.806 9 0.018 6 636 649 7 LLLASNYLSGNVPSELGSCK 2 122.085 0 2 122.083 3 −0.001 7 431 450 8 LENFPMVHSCPTTRIYSGK 2 196.057 6 2 196.113 3 0.055 7 636 654 9 MHHHHHHSSNDEVAGLLAFK 2 320.078 9 2 320.085 2 0.006 3 1 20 10 SFLVSCNHLAHVNLSHNSIPGGIFR 2 776.410 2 2 776.460 4 0.050 2 122 146 11 YENNSGLCGVPLAPCGSGHRPASSYTR 2 907.326 2 2 907.354 0 0.027 8 765 791 12 RLSVLDLSYNLFSGEIPSSFVANSPPSLK 3 137.651 9 3 137.711 9 0.060 0 200 228 13 LSVLDLSYNLFSGEIPSSFVANSPPSLK 2 981.550 8 2 981.562 3 0.011 5 201 228 14 GNLFSAGDLSATSVCALETLDLSSNNISDPLPGK 3 463.689 7 3 463.699 2 0.009 5 88 121 15 QLYLAYNQFLGDIPPELSQACGTLQELDLSGNR 3 723.832 3 3 723.931 6 0.099 3 304 336 16 HLDLSHNNFSGTFSSLDFGHCGNLTLFNVSQNR 3 735.735 8 3 735.828 4 0.092 6 229 261 -
信号肽预测结果表明:JcBRL3蛋白存在信号肽结构,切割位点位于第24位与第25位氨基酸之间(图3A)。跨膜结构预测结果表明:JcBRL3属于跨膜蛋白,具有1个跨膜区,位于第813至第835氨基酸处,推测该蛋白可能定位至细胞膜上,作为膜受体蛋白参与信号转导(图3B)。磷酸化位点分析表明:JcBRL3蛋白有101个丝氨酸(Ser)、9个酪氨酸(Tyr)和21个苏氨酸(Thr)磷酸化位点(图4A)。Uniport数据库分析表明:JcBRL3蛋白结构域位于898~1 175位氨基酸之间,为丝氨酸/苏氨酸(Serine/Threonine Kinase)活性位点蛋白激酶家族成员。蛋白二级结构分析发现:JcBRL3蛋白二级结构主要为无规则卷曲和α螺旋,α螺旋占比25.06%,无规则卷曲占比56.27%,延伸链占比18.67%。(图4B)。蛋白三维结构分析发现:JcBRL3蛋白的三维结构呈弯曲螺旋管状,是个同源二聚体,以同源二聚体的形式行使功能(图4C)。
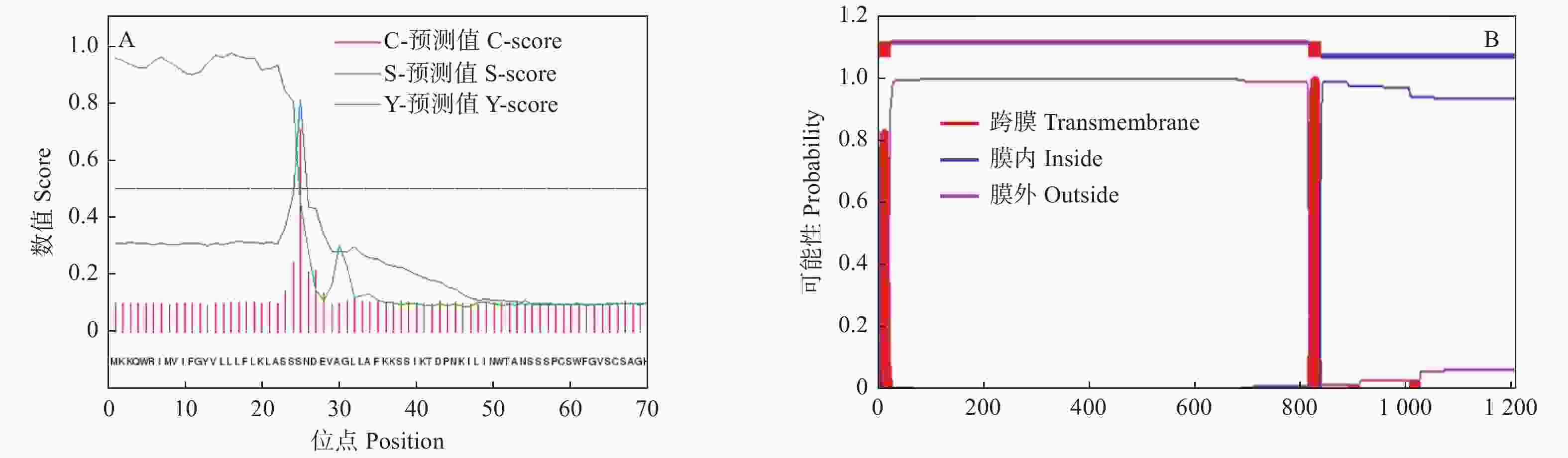
图 3 JcBRL3蛋白信号肽(A)和跨膜结构(B)预测
Figure 3. Signal peptide (A) and transmembrane structure (B) prediction of JcBRL3 protein
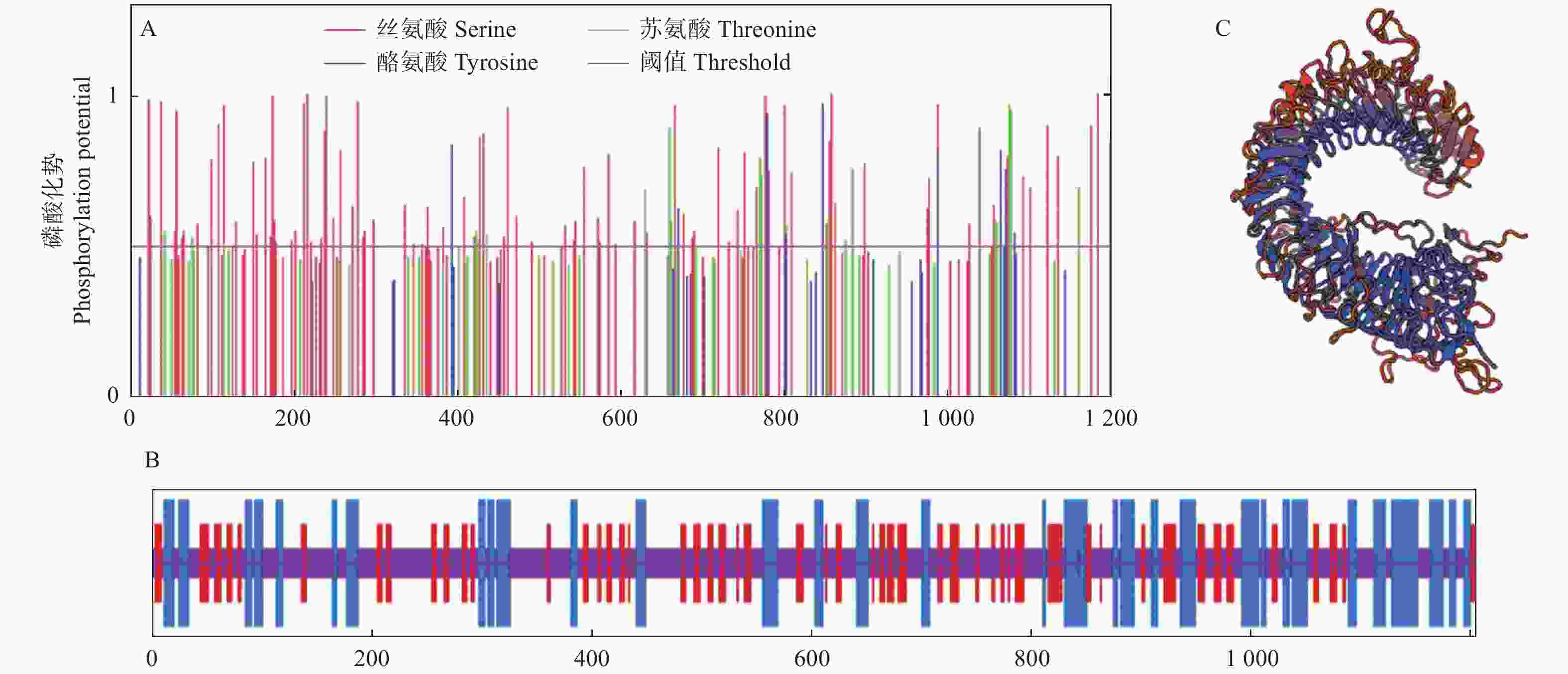
图 4 JcBRL3蛋白磷酸化位点(A)、二级结构(B)和三级结构预测图(C)
Figure 4. Prediction of phosphorylation site (A), secondary structure (B) and tertiary structure (C) of JcBRL3 protein
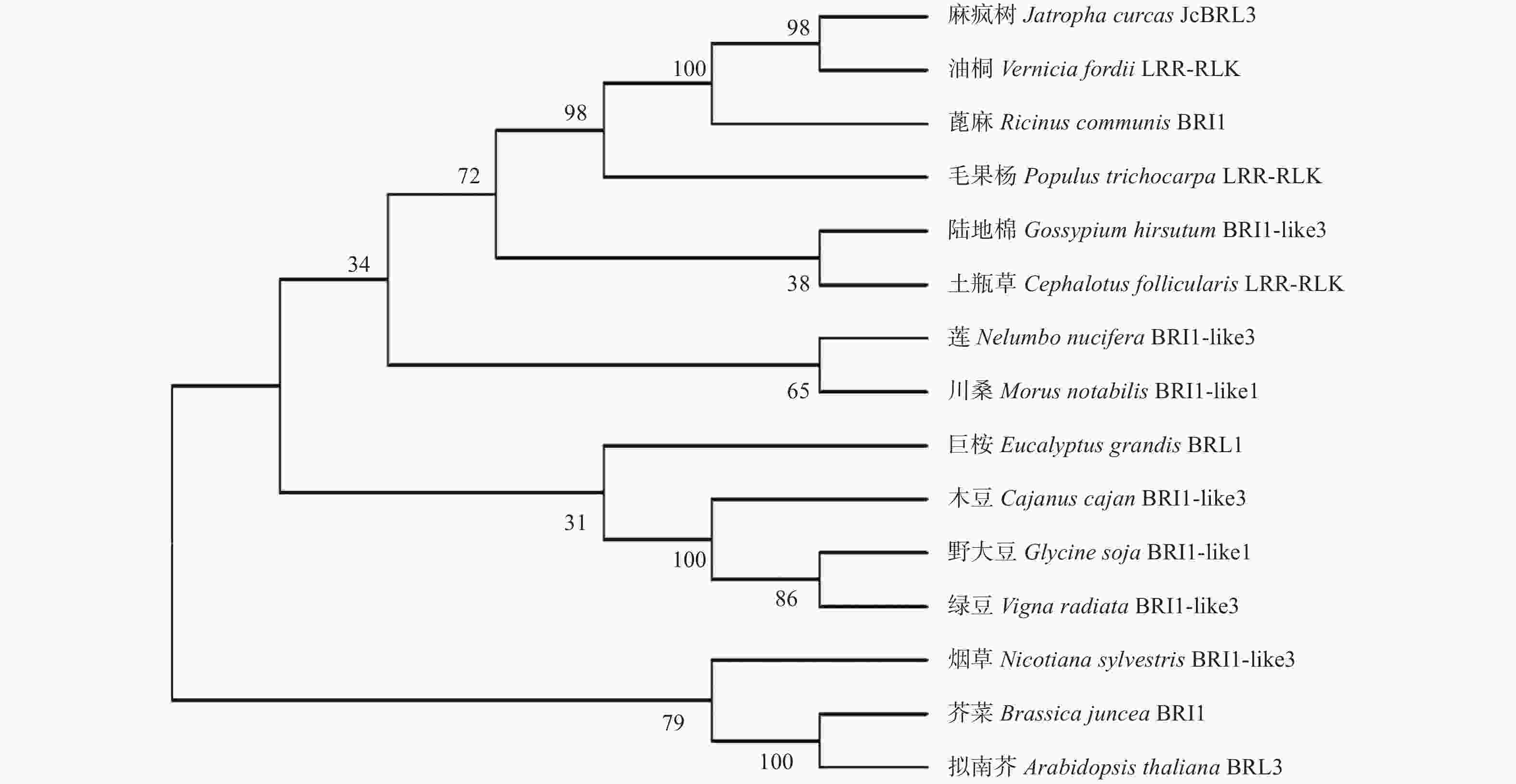
氨基酸序列分析表明:JcBRL3蛋白含有多个富含亮氨酸重复序列(LRR),并且具有保守重复序列:LxxLxLxxN/CxL,属于富含亮氨酸重复序列类受体蛋白激酶(LRR-RLK)(图5)。对其功能域氨基酸序列多重比对分析发现:JcBRL3蛋白与蓖麻(Ricinus communis L.)和亚洲棉(Gossypium arboreum L.)的BRI1蛋白相似性分别达94.6%和93.5%,与油桐(Vernicia fordii)的一个LRR-RLK相似性高达96.8%,表明JcBRL3蛋白可能与它们具有相似的结构(图6)。此外,系统发育树结果显示:JcBRL3与油桐的一个LRR-RLK蛋白聚集在同一个分支上,表明二者具有较高的同源性(图7)。
-
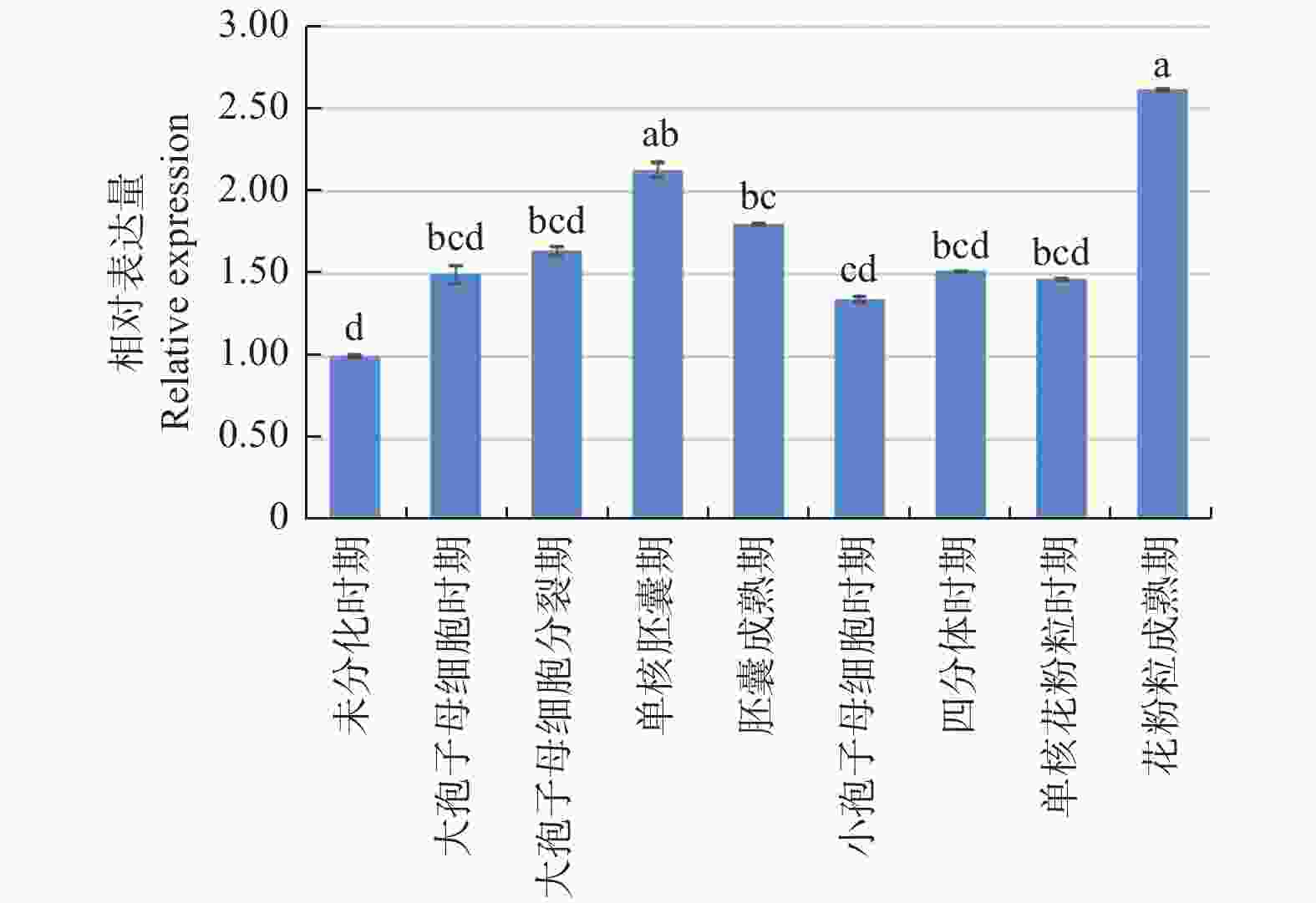
通过qRT-PCR技术检测了JcBRL3基因在麻疯树9个关键花发育时期的相对表达量。结果显示:JcBRL3基因的表达量在雌花中呈现先上升后下降的趋势,其中,在大孢子母细胞时期表达水平最低,在单核胚囊期时表达量达到最高;JcBRL3基因的表达量在雄花中则呈现先上升,后下降,最后再上升的趋势,其中在小孢子母细胞时期表达量最低,在花粉粒成熟期表达量达到最大且高于其它任何时期(图8)。这些分析结果表明JcBRL3基因很可能参与了麻疯树的雌花单核胚囊期发育和雄花花粉粒的成熟过程。
-
采用叶盘法侵染K326烟草,经卡那霉素筛选、共培养、选择培养、继代培养及生根培养等过程,成功获得了一批转基因烟草。以转基因烟草基因组DNA为模板进行PCR扩增,结果显示:野生型烟草未检测到目的条带,9株转基因植株能成功检测到目的条带,推断麻疯树JcBRL3基因已成功导入K326烟草基因组中(图9A)。提取了转基因烟草的总RNA合成cDNA第一链,通过RT-PCR扩增表明,JcBRL3基因在转基因烟草中成功表达(图9B)。
-
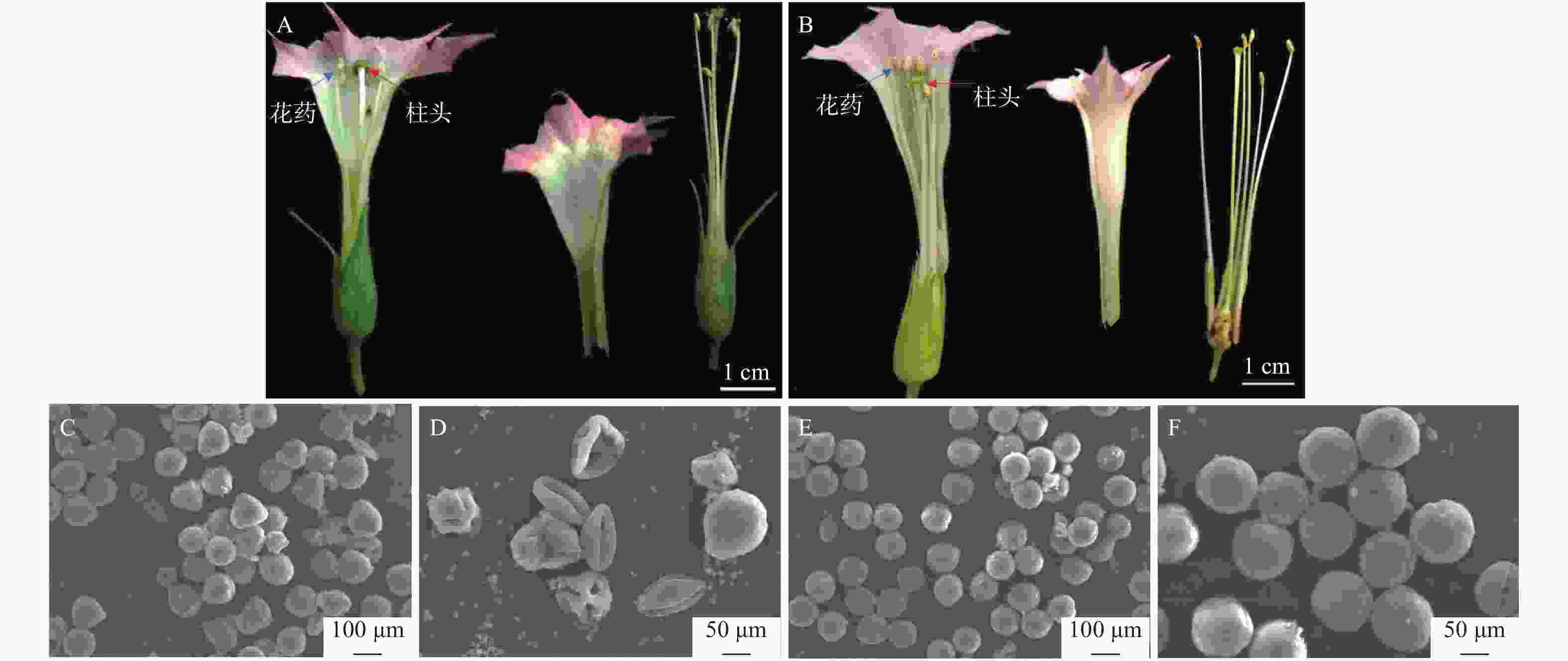
为了进一步研究JcBRL3基因在花发育的作用,对2株野生型和3株转基因烟草的花和花粉进行形态结构分析。经观察发现:2株野生型K326烟草柱头的位置均高于花药,而3株转基因烟草的柱头的位置均低于花药(图10A、B)。扫描电镜观察发现:2株野生型烟草花粉部分凹陷空瘪,平均畸形率为25.4%(图10C、D),而3株转基因烟草花粉粒基本较为饱满,凹陷空瘪较少,平均畸形率仅为7.1%(图10E、F)。推测JcBRL3基因可能参与了麻疯树雄花发育。
-
BR是一种高活性的植物激素,广泛存在于各种植物中。BR能调控植物细胞伸长和分裂、维管组织分化、种子萌发和成熟、叶片的形态建成和衰老、生殖发育等一系列植物生长发育过程,还具有增强植物抵抗低温、高温、高盐等非生物逆境的能力[14-15]。在BR信号传导过程中,首先细胞膜表面受体BRI1和辅助受体BAK1(BRI1-associated receptor kinase 1)互作形成具有活性的复合物识别BR信号;之后BR信号途径通过一系列磷酸化和去磷酸化作用,使BZR1(brassinozole-resisent 1)和BES1(BRI1-EMS-SUPOPRESSOR 1)等转录因子被激活,从而调控BR应答相关基因的表达[16]。而BRL3受体作为BRI1受体蛋白家族成员,也参与了BR的信号转导[17]。
本研究从麻疯树花发育的转录组中筛选到一个性别差异表达的油菜素内酯受体蛋白基因BRL3,其开放阅读框长3 618 bp,编码1 205个氨基酸。对其原核表达产物质谱鉴定及蛋白结构分析表明:JcBRL3蛋白包含1个胞内功能域、1个跨膜区以及1个胞外富亮氨酸重复序列结构,且胞内区具有丝氨酸/苏氨酸活性位点,这与LRR-RLK的结构一致[18],初步判定JcBRL3蛋白是一个LRR-RLK类受体激酶。在三维结构上JcBRL3与拟南芥BRI1-like1高度相似;在功能域上JcBRL3蛋白与亚洲棉BRI1蛋白、蓖麻BRI1蛋白及油桐的一个LRR-RLK序列相似性极高,这些结果表明JcBRL3蛋白很可能属于BRI1家族蛋白。
目前,对于BRL3基因的研究还十分有限,且大都集中于韧皮部形成、维管分化及抗旱性方面[19-20],其参与生殖发育调控的研究尚未涉及。本研究通过对JcBRL3基因在麻疯树花发育过程中的表达模式分析发现,JcBRL3的表达水平在麻疯树雄花花粉粒成熟期达到最高,表明其可能参与了雄花花粉粒成熟的过程;将JcBRL3基因导入烟草中过量表达发现,野生型烟草柱头位置高于花药,而转基因烟草柱头位置低于花药,且其花粉粒较饱满畸形率低,推测这种差异可能是JcBRL3基因参与烟草雌蕊发育导致的。虽然目前的研究尚未直接表明BRL3能调控雄蕊发育,但大量研究证明BR在植物雄性器官发育方面有不可替代的作用。BR能促进番茄[21]、扁桃(Prunus dulcis L.)[22]、水稻(Oryza sativa L.)[23]及拟南芥[24]等植物的花粉萌发,而BR信号传导或生物合成缺陷会导致花粉发育缺陷和雄蕊缩短[25]。BR缺陷与不敏感株系如:cpd、dwf4和bri1皆表现为雄性不育[26-27],而导致这类植株雄性不育的主要原因是花丝变短[28]、花粉数量减少以及绒粘层和小孢子发育异常[25]。此外,研究发现,在拟南芥中BR可以通过控制MS1、MS2、MYB103、TDF1和SPL/NZZ基因的表达来调控雄蕊的发育,这种调控能够完成的关键在于这些基因的启动子上含有BES1转录因子的结合位点[25]。已有研究证明BRL3基因的表达能修复bri1突变体的表型缺陷[7],并发现BES1转录因子能与BRL3启动子上的BRRE相结合从而调控BRL3[19],这暗示BRL3的表达很可能通过调控雄蕊发育来修复bri1突变体的雄性不育。因此,推测在烟草、拟南芥和麻疯树中极可能存在相同的BR调控途径,JcBRL3基因的过量表达导致烟草花丝伸长、花粉粒畸形率降低是很明显的BR增强表型,这种BR增强型很可能是由BES1转录因子的调控导致的,而这种推测是否属实还需进一步研究证明。
-
本研究通过RACE PCR技术成功从麻疯树花蕾中获得了JcBRL3基因的cDNA全长序列,该基因开放阅读框长3 618 bp,编码1 205个氨基酸;原核表达产物为JcBRL3蛋白,预测属于跨膜蛋白,含有多个LLR;qRT-PCR分析表明,其可能参与了麻疯树雌花单核胚囊期和雄花花粉粒成熟的发育过程;此外,其转基因烟草花药位置高于柱头,花粉粒也较为饱满,进一步表明JcBRL3可能参与了麻疯树雄花发育。而关于JcBRL3和其介导的BR信号是如何参与调控麻疯树花发育的还需进一步的研究来揭示。
麻疯树JcBRL3基因的克隆及在花发育过程中的功能分析
Cloning and Functional Analysis of JcBRL3 Gene from Jatropha curcas During Flower Development
-
摘要:
目的 探究BRL3基因在麻疯树花发育中的功能。 方法 利用RACE PCR技术成功从麻疯树花蕾中获得了JcBRL3基因的cDNA全长序列;利用原核表达体系对JcBRL3基因进行诱导表达,利用LC-MS/MS对其表达产物进行质谱鉴定,利用生物信息学方法对其蛋白质结构和基本理化性质进行分析;利用实时荧光定量PCR方法分析了JcBRL3基因在麻疯树雌雄花发育的9个关键时期的相对表达量;利用叶盘法将JcBRL3基因转化至烟草中超表达,分析超表达JcBRL3对烟草花的形态结构影响。 结果 JcBRL3基因的开放阅读框长3 618 bp,编码1 205个氨基酸。原核表达产物质谱鉴定表明:该基因编码1个JcBRL3蛋白(A0A067KCE7)。蛋白质结构分析表明:JcBRL3含有多个富含亮氨酸重复序列,是跨膜蛋白,并且具有保守重复序列LxxLxLxxN/CxL。荧光定量PCR分析发现:在雌花中JcBRL3的表达于单核胚囊期达到最高水平,在雄花中JcBRL3的表达于花粉粒成熟期达到最高水平且其显著高于其它任何时期。转基因烟草的花形态结构分析表明:转JcBRL3基因烟草柱头位置低于花药,花粉粒畸形率较低。 结论 JcBRL3蛋白为富亮氨酸重复序列类受体激酶蛋白,是一个膜蛋白,JcBRL3基因可能参与了麻疯树雌花单核胚囊期和雄花花粉粒成熟的发育并促进了花丝伸长。 Abstract:Objective To explore the function of BRL3 gene in flower development of Jatropha curcas. Method The full-length cDNA sequence of JcBRL3 gene was obtained by RACE PCR. The prokaryotic expression system was used to induce the expression of JcBRL3 gene. The expression products were identified by mass spectrometry using LC-MS/MS. The structure and basic physicochemical properties of the protein were analyzed by bioinformatics. The relative expression levels of JcBRL3 gene during the key stages of flower development of Jatropha curcas were analyzed by qRT-PCR. The overexpression JcBRL3 gene was transformed into tobacco by leaf plate method to analyze the influence of overexpression of JcBRL3 gene on the morphology and structure of tobacco flowers. Result The length of the open reading frame of JcBRL3 gene was 3 618 bp and encoded 1 205 amino acids. The results of mass spectrometry showed that the expression of this gene encoded a JcBRL3 protein. Protein structure analysis showed that JcBRL3 protein was a transmembrane protein with multiple leucine-rich repeats and conserved repeats: LxxLxLxxN/CxL. qRT-PCR analysis showed that the expression of JcBRL3 in female flowers reached the highest level at mononuclear embryo sac stage, and in male flowers reached the highest level at pollen grain maturation stage, which was significantly higher than at any other stage. The morphological structure analysis of transgenic tobacco flower showed that the stigma position of transgenic tobacco was lower than that of anther, and the malformation rate of pollen grains was lower. Conclusion JcBRL3 protein is a LRR-RLK, which is a membrane protein. JcBRL3 gene may participate in the development process of female flower mononuclear embryo sac stage and pollen grain maturation of male flower and promote filament elongation in Jatropha curcas. -
Key words:
- Jatropha curcas
- / flower development
- / JcBRL3
- / functional analysis
-
表 1 本研究所用引物及其序列
Table 1. Primers sequences and ways of use in this study
引物
Primers引物序列
Sequence(5′→3′)引物用途
Usage3′GSP GATTACGCCAAGCTTGGCTTCTTCCAGTAATGATGAAGTTGC 全长克隆 5′GSP GATTACGCCAAGCTTCAGTATTTGTGAGGTTGAGGGCAGTAA 全长克隆 UPM CTAATACGACTCACTATAGGGCAAGCAGTGGTATCAACGCAGAGT 全长克隆 JcBRL3-F GGAATTCCATATGCAGTAATGATGAAGTTGCGGGGTTA 原核表达载体构建 JcBRL3-R CCCAAGCTTAGAGAGATTGTTGTTAGAGACATCA 原核表达载体构建 QJcBRL3-F GCTTGACTTGAACAGCAACGACCTT 荧光定量PCR QJcBRL3-R TCCTGACACAACGCCTGGAACAAT 荧光定量PCR JcActin-F TCCCTGGTATTGCTGACCGTAT 荧光定量PCR(内参基因) JcActin-R TGGACAATGGATGGACCAGACT 荧光定量PCR(内参基因) JcTubulin-F CTCTGCAACTATGAGTGGTGTAACG 荧光定量PCR(内参基因) JcTubulin-R CACGAGAAGTAAGTGGGGCAAA 荧光定量PCR(内参基因) GMJcBRL3-F CAGTGGTCTCACAACATGAAGAAACAATGGAGAAT 过表达载体构建 GMJcBRL3-R CAGTGGTCTCATACATCATGAACTTTGAGATTCTT 过表达载体构建 JcBRL3st-F TGCCTGACCTCATCGCTGCTT 转基因烟草检测 JcBRL3st-R CCTGACACAACGCCTGGAACAA 转基因烟草检测 表 2 16条匹配肽段
Table 2. 16 matched peptide segments
编号
Number肽段
Sequence分子量
Molecular weight/Da误差
Error(± Da)起始序列
Start sequence终止序列
Terminator sequence估算值
Estimated value观测值
Observed value1 NEGGTSCR 880.357 7 880.379 8 0.022 1 613 620 2 GAGGLVEFEGIR 1 204.632 1 1 204.646 0 0.013 9 621 632 3 FCTSSNPSALQK 1 339.631 1 1 339.645 9 0.014 8 419 430 4 FSGNLETIPLSCK 1 465.735 6 1 465.740 8 0.005 2 187 199 5 FSGNLETIPLSCKR 1 621.836 7 1 621.854 5 0.017 8 187 200 6 LENFPMVHSCPTTR 1 688.788 3 1 688.806 9 0.018 6 636 649 7 LLLASNYLSGNVPSELGSCK 2 122.085 0 2 122.083 3 −0.001 7 431 450 8 LENFPMVHSCPTTRIYSGK 2 196.057 6 2 196.113 3 0.055 7 636 654 9 MHHHHHHSSNDEVAGLLAFK 2 320.078 9 2 320.085 2 0.006 3 1 20 10 SFLVSCNHLAHVNLSHNSIPGGIFR 2 776.410 2 2 776.460 4 0.050 2 122 146 11 YENNSGLCGVPLAPCGSGHRPASSYTR 2 907.326 2 2 907.354 0 0.027 8 765 791 12 RLSVLDLSYNLFSGEIPSSFVANSPPSLK 3 137.651 9 3 137.711 9 0.060 0 200 228 13 LSVLDLSYNLFSGEIPSSFVANSPPSLK 2 981.550 8 2 981.562 3 0.011 5 201 228 14 GNLFSAGDLSATSVCALETLDLSSNNISDPLPGK 3 463.689 7 3 463.699 2 0.009 5 88 121 15 QLYLAYNQFLGDIPPELSQACGTLQELDLSGNR 3 723.832 3 3 723.931 6 0.099 3 304 336 16 HLDLSHNNFSGTFSSLDFGHCGNLTLFNVSQNR 3 735.735 8 3 735.828 4 0.092 6 229 261 -
[1] Vert G, Jaillais Y. Brassinosteroid signaling and BRI1 dynamics went underground[J]. Current Opinion in Plant Biology, 2016, 33: 92-100. doi: 10.1016/j.pbi.2016.06.014 [2] 郑 洁, 王 磊. 油菜素内酯在植物生长发育中的作用机制研究进展[J]. 中国农业科技导报, 2014, 16(1):52-58. [3] Li J, Wen J, Lease K A, et al. BAK1, an Arabidopsis LRR receptor-like protein kinase, interacts with BRI1 and modulates brassinosteroid signaling[J]. Cell, 2002, 110(2): 213-22. doi: 10.1016/S0092-8674(02)00812-7 [4] Li J, Chory J. A putative leucine-rich repeat receptor kinase involved in brassinosteroid signal transduction[J]. Cell, 1997, 90(5): 929-938. doi: 10.1016/S0092-8674(00)80357-8 [5] Vert G, Nemhauser J L, Geldner N, et al. Molecular mechanisms of steroid hormone signaling in plants[J]. Annual Review of Cell & Developmental Biology, 2005, 21(1): 177-201. [6] He Z, Wang Z Y, Li J, et al. Perception of brassinosteroids by the extracellular domain of the receptor kinase BRI1[J]. Science, 2000, 288(5475): 2360-2363. doi: 10.1126/science.288.5475.2360 [7] Cañodelgado A, Yin Y, Yu C, et al. BRL1 and BRL3 are novel brassinosteroid receptors that function in vascular differentiation in Arabidopsis[J]. Development, 2004, 131(21): 5341-5351. doi: 10.1242/dev.01403 [8] Zhou A, Wang H, Walker J C, et al. BRL1, a leucine-rich repeat receptor-like protein kinase, is functionally redundant with BRI1 in regulating Arabidopsis brassinosteroid signaling[J]. Plant Journal, 2004, 40(3): 399-409. doi: 10.1111/j.1365-313X.2004.02214.x [9] Nie S, Huang S, Wang S, et al. Enhancing brassinosteroid signaling via overexpression of tomato (Solanum lycopersicum) SlBRI1 improves major agronomic traits[J]. Frontiers in Plant Science, 2017, 8: 1386. doi: 10.3389/fpls.2017.01386 [10] Singh A, Breja P, Khurana J P, et al. Wheat Brassinosteroid-Insensitive1 (TaBRI1) interacts with members of TaSERK gene family and cause early flowering and seed yield enhancement in Arabidopsis[J]. PLoS One, 2016, 11(6): e0153273. doi: 10.1371/journal.pone.0153273 [11] 雷世康, 徐 刚. 麻疯树BRI1基因的鉴定及其在不同发育时期花蕾中的表达分析[J]. 林业科学研究, 2019, 32(5):121-129. [12] Wu W G, Huang J K, Deng X Z. Potential land for plantation of Jatropha curcas as feedstocks for biodiesel in China[J]. Science China-Earth Sciences, 2009, 53(1): 120-127. [13] 郭承刚, 王朝文, 李建富, 等. 麻疯树物候期和花的发育动态观察[J]. 现代农业科技, 2007(1):12-13. doi: 10.3969/j.issn.1007-5739.2007.01.006 [14] 李元元, 曹清河. 油菜素内酯参与调控植物生长发育与抗逆性的机制及其育种应用研究[J]. 中国农业科技导报, 2015, 17(2):25-32. [15] Planas-Riverola A, Gupta A, Betegón-Putze I, et al. Brassinosteroid signaling in plant development and adaptation to stress[J]. Development, 2019, 146(5): dev151894. doi: 10.1242/dev.151894 [16] 王 喆, 王 璐, 宋旭明, 等. 植物油菜素内酯信号通路与植物免疫相关研究进展[J]. 安徽农业科学, 2019, 47(4):26-29. doi: 10.3969/j.issn.0517-6611.2019.04.006 [17] Lozano-Elena F, Cao-Delgado A I. Emerging roles of vascular brassinosteroid receptors of the BRI1-like family[J]. Current Opinion in Plant Biology, 2019, 51: 105-113. doi: 10.1016/j.pbi.2019.06.006 [18] Shiu S H, Bleecker A B. Plant receptor-like kinase gene family: diversity, function, and signaling[J]. Science's STKE:signal transduction knowledge environment, 2001, 2001(113): re22. [19] Salazar-Henao J E, Lehner R, Betegón-Putze I, et al. BES1 regulates the localization of the brassinosteroid receptor BRL3 within the provascular tissue of the Arabidopsis primary root[J]. Journal of Experimental Botany, 2016, 67(17): 4951-4961. doi: 10.1093/jxb/erw258 [20] Fàbregas N, Lozano-Elena F, Blasco-Escámez D, et al. Overexpression of the vascular brassinosteroid receptor BRL3 confers drought resistance without penalizing plant growth[J]. Nature communications, 2018, 9(1): 4680. doi: 10.1038/s41467-018-06861-3 [21] Singh I, Shono M. Physiological and molecular effects of 24-Epibrassinolide, a brassinosteroid on thermotolerance of tomato[J]. Plant Growth Regulation, 2005, 47(2-3): 111-119. doi: 10.1007/s10725-005-3252-0 [22] Sotomayor C, Castro J, Velasco, Nicolás, et al. Influence of seven growth regulators on fruit set, pollen germination and pollen tube growth of almonds[J]. Journal of Agricultural Science & Technology B, 2012(9): 1051-1056. [23] Thussagunpanit J, Jutamanee K, Chai-arree W, et al. Increasing photosynthetic effificiency and pollen germination with 24-Epibrassinolide in rice (Oryza sativa L.) under heat stress[J]. Thai Journal of Botany 4, 2012: 1135-143. [24] Vogler F, Schmalzl C, Englhart M, et al. Brassinosteroids promote Arabidopsis pollen germination and growth[J]. Plant Reproduction, 2014, 27(3): 153-167. doi: 10.1007/s00497-014-0247-x [25] Ye Q, Zhu W, Li L, et al. Brassinosteroids control male fertility by regulating the expression of key genes involved in Arabidopsis anther and pollen development[J]. Proceedings of the National Academy of Sciences of the United States of America, 2010, 107(13): 6100-6105. doi: 10.1073/pnas.0912333107 [26] Hong Z, Ueguchi-Tanaka M, Shimizu-Sato S, et al. Loss-of-function of a rice brassinosteroid biosynthetic enzyme, C-6 oxidase, prevents the organized arrangement and polar elongation of cells in the leaves and stem[J]. Plant Journal, 2002, 32(4): 495-508. doi: 10.1046/j.1365-313X.2002.01438.x [27] Hewitt F R, Hough T, O’ Neill P, et al. Effect of brassinolide and other growth regulators on the germination and growth of pollen tubes of Prunus avium using a multiple hangingdrop assay[J]. Plant Physiology, 1985, 1: 201-211. [28] Kim T W, Hwang J Y, Kim Y S, et al. Arabidopsis CYP85A2, a cytochrome P450, mediates the Baeyer-Villiger oxidation of castasterone to brassinolide in brassinosteroid biosynthesis[J]. The Plant Cell, 2005, 17(8): 2397-2412. doi: 10.1105/tpc.105.033738 -



 下载:
下载: